如何分析qPCR数据?你的实验结果是这样分析的吗? |
您所在的位置:网站首页 › pcr扩增实验报告结果分析图 › 如何分析qPCR数据?你的实验结果是这样分析的吗? |
如何分析qPCR数据?你的实验结果是这样分析的吗?
|
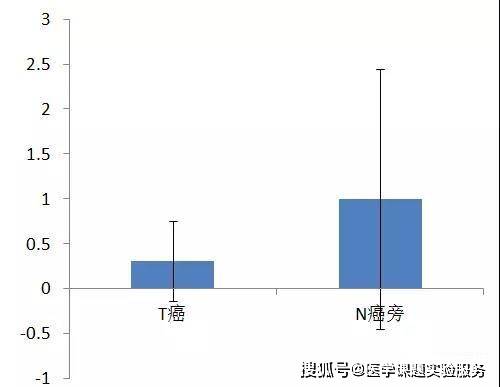
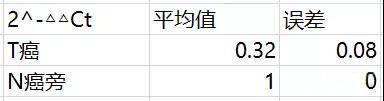
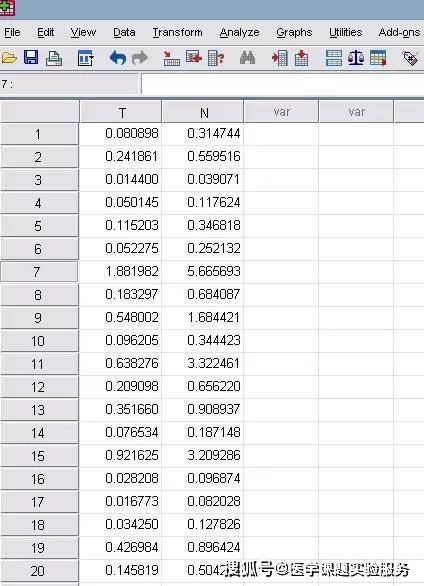
按照上一次案例1里面的统计方法去画图, 如果我们按照上一次案例1里面的统计方法去做,先求出N(癌旁)2^-△Ct的平均值n1,然后用T(癌) 2^-△Ct分别除以n1,再用每个N(癌旁)2^-△Ct处理n1,就得到了最终可以统计的结果T(癌) 2^-△△Ct,和N(癌旁)2^-△△Ct,具体计算过程就不罗列了,整理结果如下:
如果接着作图,会出现如下结果:
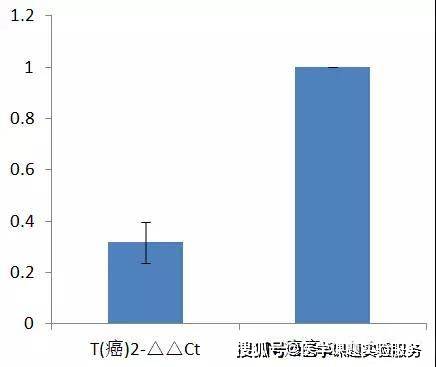
你是不是吓一跳,癌和癌旁是不是没差异了? 但是仔细一看,从数据角度看来所有的癌里面A的表达水平都比癌旁低啊,为什么做到这个图上面,看上去这么不可能呢。 那么问题究竟出在哪里呢?首先上一节中我们是三次重复试验,对于同一种药物作用于同一种细胞相同的时间,理论上三次独立重复试验中药物引起p53 mRNA水平的变化是确定的,而在本案例中,不同病人之间的标本不能算作是实验重复,不同个体之间的A基因mRNA水平也是不一样的。因此,不能采用案例1中的计算方式。 下面首先介绍下我们常用的模式: 我们用每组的T(癌) 2^-△Ct除以N(癌旁)2^-△Ct,得到T(癌) 2^-△△Ct,这样一来,N(癌旁)2^-△△Ct都为1,然后整理结果得到如下:
然后作图得到如下:
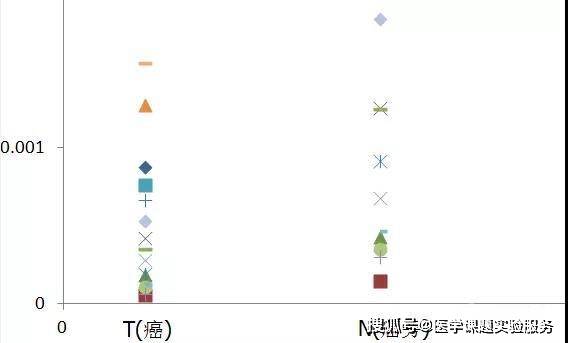
这个是不是比第一次柱形图好看? 但是这种做法其实是有问题的,虽然看上去差异比较大(通过统计计算差异也比较大),但是N(癌旁)已经没有误差,这是不科学的。 所以在本文中,我们以T(癌) 2^-△C和N(癌旁)2^-△Ct做成散点图,如下所示(注意不是△△):
把Y轴调整下如下:
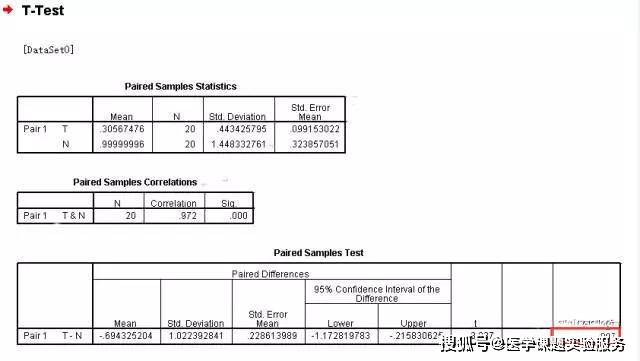
可以看出,在癌旁组散点图位置均上移。我们通过SPSS软件统计分析两组之间的差异:
采用配对T检验(T检验的前提是样本服从正态分布,可以提前检测下,一般测定某一个蛋白或者mRNA的水平,可以看作是正态分布)。
p=0.007, 具有显著性差异。 本次文章转自医学实验小坑,如果觉得有帮助欢迎收藏转发~ 关注“医学课题实验服务”,为你搜集分享更多学习干货。返回搜狐,查看更多 |
【本文地址】
今日新闻 |
点击排行 |
|
推荐新闻 |
图片新闻 |
|
专题文章 |